PAR-CLIP-seq:描绘RNA-蛋白质相互作用图谱
项目简介
PAR-CLIP-seq(Photoactivatable Ribonucleoside-Enhanced Crosslinking and lmmunoprecipitation sequencing)即基于光活化核糖核苷的交联和免疫沉淀测序技术[1],将具有光活性的核糖核苷类似物4sU掺入到新转录的RNA中,再通过分析碱基T-C转换位点,可在全转录组范围内研究RNA与蛋白的相互作用,揭示靶向RBP的RNA结合位点。
技术优势
1.紫外交联效率高,是CLIP-seq的100~1,000倍
2.分辨率高,定位到结合位点
3.特异性高
技术应用
1.鉴定全转录组RNA与蛋白质直接结合位点
2.揭示全转录组RNA—蛋白质相互作用
送样要求
≥3*107个细胞/样本
样本类型:活细胞
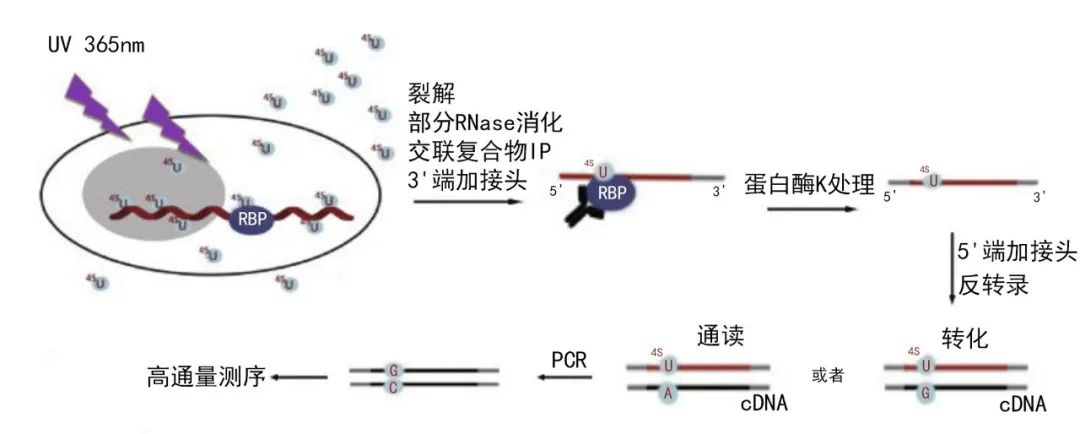
Ribo-seq 技术流程[2]
技术原理
将具有光活性的核糖苷类似物4sU插入到活细胞的新生RNA转录本中,在365nm紫外灯辐射的细胞中4sU标记的RNA被诱导与RBP相互作用;免疫共沉淀所要的RBP,然后分离被交联和共沉淀的RNA。RNA随即被转换成cDNA文库并且进行深入测序。4sU的处理令交联的序列产生T-C的转变,因此通过PAR-CLIP所准备的cDNA文库能够准确的定位交联的位置。
分析内容
1.原始数据质控、过滤
2.参考基因组比对
3.Peak calling
4.Peak注释
5.GO富集分析5.KEGG富集分析
6.Motif分析
7.信号矩阵分析(Peak热图)
8.CIMS 分析
9.可视化文件
10.差异分析(若有多组样品可找出差异结合位点)

图1. IGV峰图
结果示例

图2. Motif分析[2]
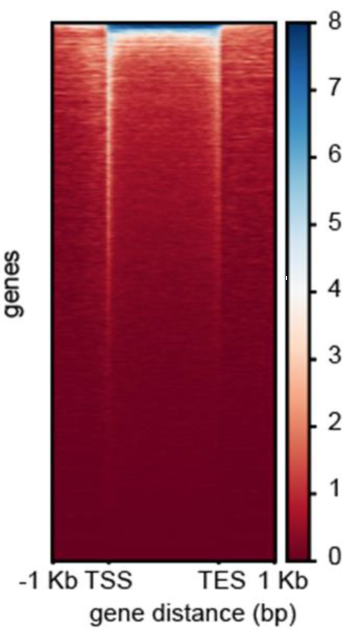
图3. 信号分布热图
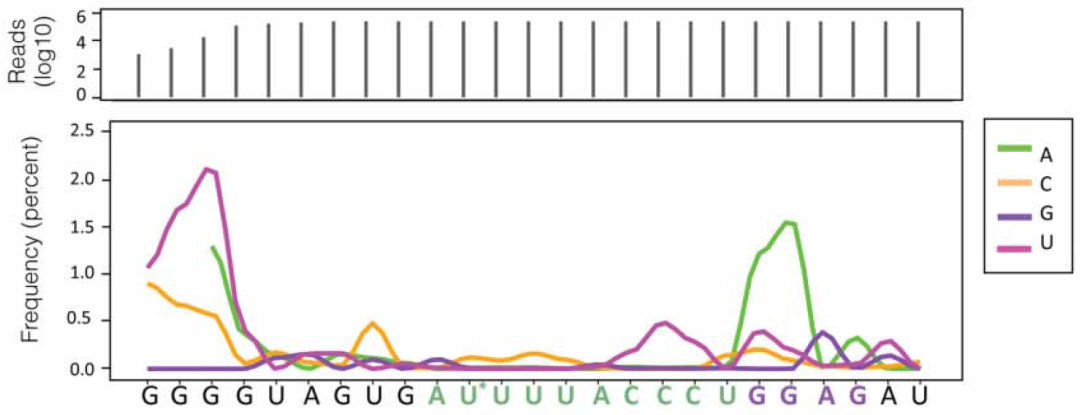
图4. CIMS分析突变频率[3]
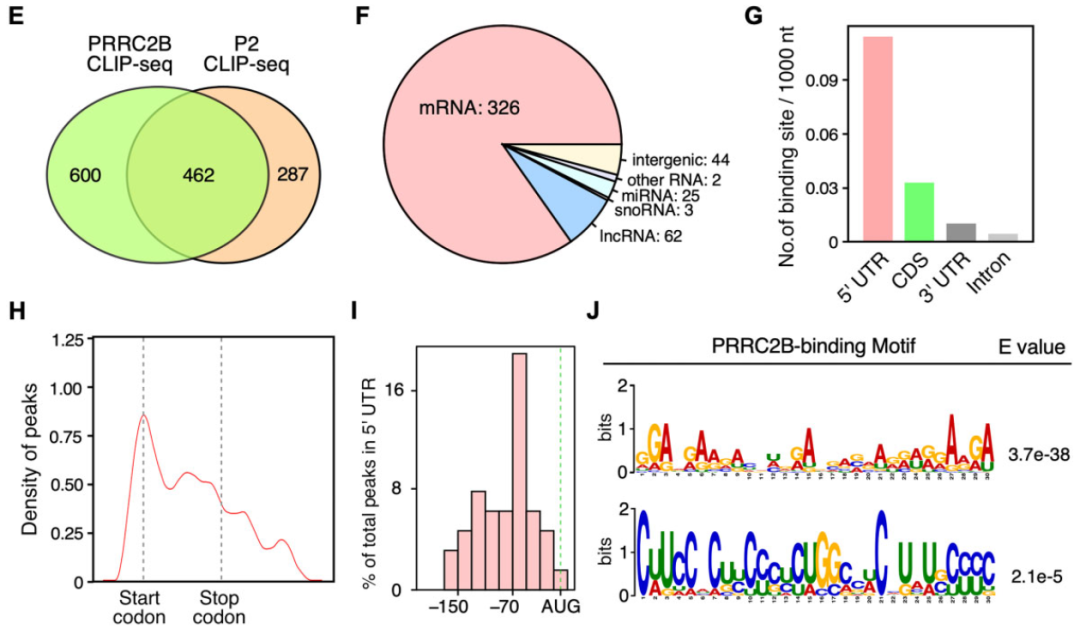
图5. PAR-CLIP-seq结果显示 PRRC2B -mRNA相互作用
案例:
NAR:RNA 结合蛋白 PRRC2B 介导特定 mRNA 的翻译并调节细胞周期进程[4]
越来越多的证据表明,基因表达的转录后控制,包括 RNA 剪接、运输、修饰、翻译和降解,主要依赖于 RNA 结合蛋白 (RBP)。然而,许多 RBP 的功能仍未得到充分研究。此研究中鉴定了一种新 RBP——PRRC2B的功能。通过PAR-CLIP-seq,研究者在HEK293T 细胞中一组特定 mRNA上的翻译起始密码子附近鉴定了全转录组富含 CU-或 GA 的 PRRC2B 结合位点。后续通过更多的机制研究表明, PRRC2B 对于有效翻译细胞周期进程和细胞增殖所需的特定蛋白质至关重要。
参考文献
[1]PAR-CLIP (Photoactivatable Ribonucleoside-Enhanced Crosslinking and lmmunoprecipitation): a step-by-stepprotocol to the transc riptome - wide identification of binding sites of RNA-binding proteins. Methods Enzymol.2014:539:113-61
[2]Hou L, Wei Y, Lin Y, et al. Concurrent binding to DNA and RNA facilitates the pluripotency reprogramming activity of Sox2. Nucleic Acids Res 2020 Apr 17;48(7)
[3]Ransey E, Björkbom A, Lelyveld VS, et al. Comparative analysis of LIN28-RNA binding sites identified at single nucleotide resolution. RNA Biol 2017 Dec 02;14(12)
[4]Jiang F, Hedaya OM, Khor E, et al. RNA binding protein PRRC2B mediates translation of specific mRNAs and regulates cell cycle progression. Nucleic Acids Res 2023 Jun 23;51(11)
